bioconductor系列的包都是一样的安装方式:
source("http://bioconductor.org/biocLite.R")
biocLite("GEOquery")
以前GEO数据库主要是microarray的芯片数据,后来有了RNA-seq,如果同时做多个样品的RNA-seq,表达量矩阵后来也可以上传到GEO数据库里面,只有看到文献里面有提到GEO数据库,都可以通过这个R包俩进行批量下载,其实就是网页版的一个API调用而已:
GEO数据库里面有四种数据
At the most basic level of organization of GEO, there are four basic entity types.
The first three (Sample, Platform, and Series) are supplied by users;
the fourth, the dataset, is compiled and curated by GEO sta
from the user-submitted data.
GEO accession number (GPLxxx).
GEO accession number (GSMxxx)
GEO accession number (GSExxx).
GEO DataSets (GDSxxx)
记住大小关系:一个GDS可以有多个GSM,一个GSM可以有多个GSE,至于GPL,一般不接触的
我们通常接触的都是GSE系列(一个GSE里面有多个GSM)的数据,而且这个包最重要的就是一个getGEO函数。
只要你通过文献确定了你的检索号,就可以通过这个函数来下载啦
检索号一般是A character string representing a GEO object for download and
parsing. (eg., 'GDS505','GSE2','GSM2','GPL96'
这个函数有很多参数,除非你需要下载的文件,那么就设置destdir到你喜欢的目录,如果只需要表达量数据就不用了。
getGEO(GEO = NULL, filename = NULL, destdir = tempdir(), GSElimits=NULL,
GSEMatrix=TRUE,AnnotGPL=FALSE)
例如:
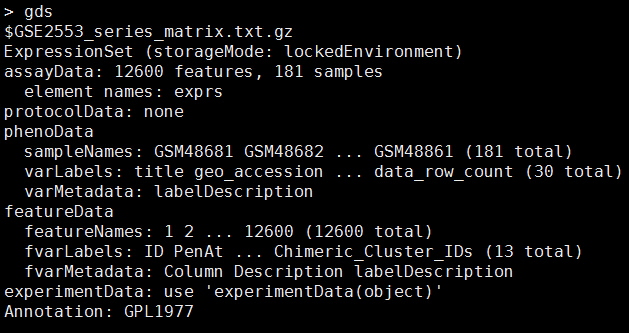
gds <- getGEO("GDS10") 会返回一个对象,而且下载数据一般会在tmp目录下面,当然如果你需要保存这些文件,你可以自己制定下载目录及文件名。
gse2553 <- getGEO("GSE2553")
GDS2eSet函数可以把上面这个下载函数得到的对象(要确定是GDS而不是GSE)变成表达对象
pData和exprs函数都可以处理上面这个表达对象,从而分别得到样品描述矩阵和样品表达量矩阵
综合一起就是
g4100 <- GDS2eSet(getGEO("GDS4100"))
g4102 <- GDS2eSet(getGEO("GDS4102"))
e4102<-exprs(g4102)
e4100<-exprs(g4100)
g4102 <- GDS2eSet(getGEO("GDS4102"))
e4102<-exprs(g4102)
e4100<-exprs(g4100)
这样的代码,这个e4100和e4102就都是一个数值矩阵啦,可以进行下游分析,但是如果是下载的GSM数据
就用下面这个代码,GSE26253_series_matrix.txt是通过GSEMatrix=TRUE这个参数特意下载到你的目录的
expr_dat=read.table("GSE26253_series_matrix.txt",comment.char="!",stringsAsFactors=F)
这样读取也是一个数值矩阵
具体大家可以看这个包的说明书
#Download GDS file, put it in the current directory, and load it:
gds858 <- getGEO('GDS858', destdir=".")
如果使用了GSEMatrix=TRUE这个参数,那么除了下载soft文件,还有表达量矩阵文件,可以直接用read.table读取那个文件。
#Or, open an existing GDS file (even if its compressed):
gds858 <- getGEO(filename='GDS858.soft.gz')
下面这个下载的是GSE对象,GDS对象还有大一点